 |
广州2021年4月6日 /美通社/ -- 基准医疗(AnchorDx)与中山大学附属第六医院的兰平教授和吴现瑞教授团队在Molecular Oncology(影响因子: 6.574)发表了一篇题为“A novel cell-free DNA methylation-based model improves the early detection of colorectal cancer”的研究论文。
结直肠癌(CRC)是全球第三大最常见的恶性肿瘤,尽管治疗方法有所改善,但TNM晚期CRC患者的预后仍较差。I期CRC患者的5年生存率为91%,而IV期仅为14%。因此,对早期CRC的精准筛查是降低CRC相关死亡率的关键策略之一。
目前,CRC筛查方法主要分为有创结肠镜检查和无创大便CRC筛查,有创结肠镜检查存在对技术和设备要求高、检查前需要彻底清洁肠道、侵入性检查会带来一定的痛苦和并发症风险、患者依从性差等问题;而无创大便CRC筛查存在假阳性率高、非必要的治疗、价格相对较高、缺乏长期随访研究数据等问题,现阶段迫切需要一种高灵敏度和特异度的无创性CRC筛查产品。
本项目研究通过187个组织DNA样本(91个非恶性组织,26个进展期腺瘤[AA]和70个CRC)和489个血浆cfDNA样本进行靶向DNA甲基化测序,建立并验证了用于AA和早期CRC非侵入性检测的基于11个DNA甲基化生物标志物的cfDNA甲基化模型。
1、研究工作流程
为鉴定结直肠癌(CRC)特异的DNA甲基化生物标志物,研究者收集了313个组织样本(139例正常,30例进展期腺瘤[AA]和144例结直肠癌[CRC])进行靶向DNA甲基化二代测序(NGS)。此外,为进一步探索这些DNA甲基化标志物在CRC早期检测中的临床应用,采集了577例血浆样本(169例健康对照组、44例非进展期腺瘤[NAA]、76例AA和288例CRC)进行NGS测序分析。经过DNA提取、文库构建和DNA甲基化测序的质控,最终分析了187个组织样本和489个血浆样本。应用Wilcoxon检验和Benjamini-Hochberg多重检验筛选组织队列,得到了667个CRC特异的DNA甲基化生物标志物。将133例正常血浆样本和248例CRC血浆样本随机分组到训练和验证集中,进行建模分析,从该667个生物标志物中进一步筛选CRC特异甲基化生物标志物。在LASSO选择后,基于训练集获得11个CRC特异性甲基化生物标志物,然后使用验证集进一步确认。最终,通过对NAA、AA和CRC患者的诊断来评估该模型的临床价值。同时,通过与癌胚抗原(CEA)和碳水化合物抗原19-9(CA19-9)方法的比较,评估了该模型在CRC管理中的稳定性。(Figure 1)
2、健康对照组、NAA、AA和CRC患者的cfDNA提取分析
比较551例(162例健康对照[正常]、44例非进展期腺瘤[NAA]、74例进展期腺瘤[AA]、69例结直肠癌I期[I]、97例结直肠癌II期[II]、70例结直肠癌III期[III]、35例结直肠癌IV期[IV])cfDNA质控合格的样本的cfDNA浓度。数据显示为平均值±标准差(SD);ns,不显著(Figure 2,***p<0.001;****p<0.0001)。
3、组织DNA甲基化图谱的表征
187个组织样本中667个结直肠癌(CRC)特异DNA甲基化生物标志物的无监督分层聚类分析(Figure 3A)。CRC、进展期腺瘤(AA)和正常样本的主成分分析(Figure 3B)。CRC与AA组甲基化模式的相关性分析(Figure 3C)。基于9921个生物标志物计算平均甲基化水平。图中的值是与正常样本共甲基化值(PCM)的比值,然后进行Log2转换来生成的。
4、cfDNA甲基化模型检测腺瘤和CRC患者的性能和风险评分
在训练和验证集中,模型的ROC曲线下面积(AUC)分别为0.90(0.85-0.94)和0.92(0.88-0.96)(Figure 4A-B)。应用于腺瘤患者的诊断时,该模型在腺瘤、非进展期腺瘤(NAA)和进展期腺瘤(AA)中分别达到0.82(0.76-0.87)、0.77(0.69-0.86)和0.85(0.78-0.91)(Figure 4C-E)。该模型在I期结直肠癌检测中的AUC为0.90(0.86-0.95)(n=199)(Figure 4F)。该模型在结直肠癌(CRC)患者的诊断中表现突出,AUC为0.91(0.88-0.94)(n=381)(Figure 4G)。在CRC和AA队列(n=449)的检测中,模型的总体AUC为0.90(0.87-0.93)(Figure 4H)。模型在健康对照(正常)和NAA、AA以及结直肠癌I-IV期患者中的风险评分(n=489,配对t检验;Figure 4I,*****p<0.0001)。
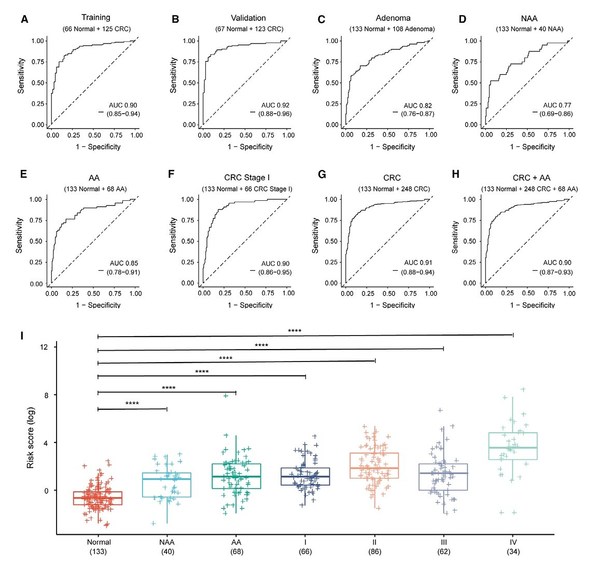
Figure 4. The performance and risk score of the cell-free DNA methylation model in detecting adenoma and CRC patients.
5、cfDNA甲基化模型与肿瘤生物标志物CEA和CA19-9的CRC诊断性能比较
cfDNA甲基化模型、癌胚抗原(CEA)和碳水化合物抗原19-9(CA19-9)检测结直肠癌(CRC)的ROC曲线下面积分别为0.91(0.88-0.94)、0.77(0.72-0.82)和0.59(0.53-0.65;Figure 5)。
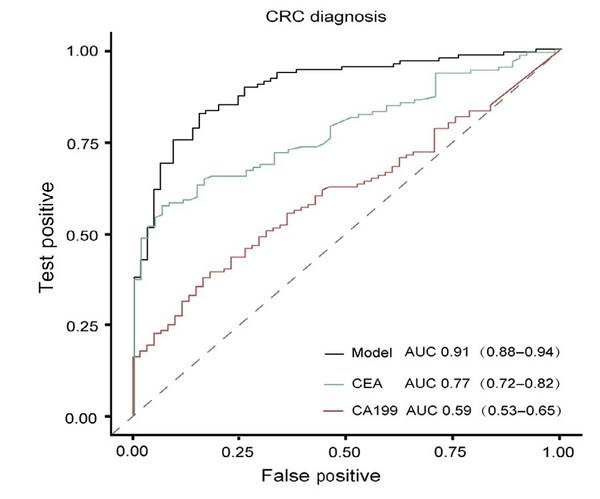
Figure 5. Comparison of CRC diagnostic performance between the cfDNA methylation model and the tumor biomarker CEA and CA19-9.
本研究建立并验证了用于AA和早期CRC非侵入性检测的基于11个DNA甲基化生物标志物的cfDNA甲基化模型。我们收集了来自CRC、进展期腺瘤(AA)、非进展期腺瘤和健康对照组的313个组织和577个血浆样本,去除质控不合格的,选择187个组织DNA样本(来自CRC患者的91个非恶性组织,26个AA和70个CRC)和489个血浆cfDNA样本进行靶向DNA甲基化测序。在训练队列中基于11个甲基化生物标志物(ROC曲线下面积[AUC]=0.90[0.85-0.94])开发了一个用于CRC检测的cfDNA甲基化模型,该模型在验证队列(AUC=0.92[0.88-0.96])中得到验证。本研究建立的cfDNA甲基化模型能够稳定地诊断出早期CRC(AUC=0.90[0.86-0.95])或AA(AUC=0.85[0.78-0.91])的患者。该模型将在CRC的早期诊断临床实践中发挥着积极作用。
原文链接:https://febs.onlinelibrary.wiley.com/doi/full/10.1002/1878-0261.12942

